Гомология последовательностей

Гомология последовательностей – это биологическая гомология между последовательностями ДНК , РНК или белков , определяемая с точки зрения общего происхождения в эволюционной истории жизни . Два сегмента ДНК могут иметь общее происхождение из-за трех явлений: либо события видообразования (ортологи), либо события дупликации (паралоги), либо события горизонтального (или латерального) переноса генов (ксенологи). [1]
Гомологию ДНК, РНК или белков обычно определяют по сходству их нуклеотидных или аминокислотных последовательностей. Значительное сходство является убедительным доказательством того, что две последовательности связаны эволюционными изменениями по сравнению с общей предковой последовательностью. Выравнивание нескольких последовательностей используется для указания того, какие области каждой последовательности являются гомологичными.
Тождество, сходство и сохранение
[ редактировать ]
Термин «процент гомологии» часто используется для обозначения «сходства последовательностей», то есть процента идентичных остатков ( процента идентичности ) или процента остатков, сохранившихся со схожими физико-химическими свойствами ( процента сходства ), например, лейцина и изолейцина . используется для «количественной оценки гомологии». На основании приведенного выше определения гомологии эта терминология неверна, поскольку сходство последовательностей — это наблюдение, а гомология — это вывод. [3] Последовательности либо гомологичны, либо нет. [3] Это означает, что термин «процент гомологии» является неправильным. [4]
Как и в случае с морфологическими и анатомическими структурами, сходство последовательностей может возникать в результате конвергентной эволюции или, как в случае с более короткими последовательностями, случайно, что означает, что они не гомологичны. Области гомологичной последовательности также называются консервативными . Это не следует путать с консервацией аминокислотных последовательностей, когда аминокислота в определенном положении заменена другой, имеющей функционально эквивалентные физико-химические свойства.
Частичная гомология может возникнуть, когда сегмент сравниваемых последовательностей имеет общее происхождение, а остальные — нет. Такая частичная гомология может возникнуть в результате слияния генов .
Ортология
[ редактировать ]
Гомологичные последовательности являются ортологичными, если предполагается, что они произошли от одной и той же предковой последовательности, разделенной событием видообразования : когда вид расходится на два отдельных вида, копии одного гена в двух полученных видах считаются ортологичными. Ортологи, или ортологичные гены, — это гены разных видов, произошедшие в результате вертикального происхождения от одного гена последнего общего предка . Термин «ортолог» был придуман в 1970 году молекулярным эволюционистом Уолтером Фитчем . [5]
Например, растительный регуляторный белок гриппа присутствует как у Arabidopsis (многоклеточное высшее растение), так и у Chlamydomonas (одноклеточные зеленые водоросли). Вариант Chlamydomonas более сложен: он пересекает мембрану дважды, а не один раз, содержит дополнительные домены и подвергается альтернативному сплайсингу. Однако он может полностью заменить гораздо более простой белок арабидопсиса , если его перенести из водорослей в геном растения с помощью генной инженерии . Значительное сходство последовательностей и общие функциональные домены указывают на то, что эти два гена являются ортологичными. [6] унаследовано от общего предка .
Ортология строго определяется с точки зрения происхождения. Учитывая, что точное происхождение генов у разных организмов трудно установить из-за событий дупликации генов и реаранжировки генома, наиболее убедительные доказательства того, что два подобных гена ортологичны, обычно обнаруживаются путем проведения филогенетического анализа линии генов. Ортологи часто, но не всегда, выполняют одну и ту же функцию. [7]
Ортологичные последовательности предоставляют полезную информацию для таксономической классификации и филогенетических исследований организмов. Характер генетической дивергенции можно использовать для отслеживания родства организмов. Два очень близкородственных организма, скорее всего, будут иметь очень схожие последовательности ДНК между двумя ортологами. И наоборот, организм, который дальше эволюционно удален от другого организма, вероятно, будет демонстрировать большее расхождение в последовательности изучаемых ортологов. [ нужна ссылка ]
Базы данных ортологичных генов
[ редактировать ]Учитывая их огромную важность для биологии и биоинформатики , ортологичные гены были организованы в несколько специализированных баз данных , которые предоставляют инструменты для идентификации и анализа ортологичных последовательностей генов. В этих ресурсах используются подходы, которые в целом можно разделить на те, которые используют эвристический анализ всех парных сравнений последовательностей, и те, которые используют филогенетические методы. Впервые методы сравнения последовательностей были применены в базе данных COGs в 1997 году. [8] Эти методы были расширены и автоматизированы в двенадцати различных базах данных, наиболее продвинутой из которых является AYbRAH Анализ дрожжей путем реконструкции происхождения гомологов. [9] а также следующие базы данных прямо сейчас.
- яйцоNOG [10] [11]
- ГринФилДБ [12] [13] для растений
- InParanoid [14] [15] фокусируется на отношениях парных ортологов
- ОХНОЛОГИ [16] [17] представляет собой хранилище генов, сохранившихся в результате дупликаций целого генома в геномах позвоночных, включая человека и мышь.
- СОБСТВЕННЫЙ [18]
- ОртоБД [19] понимает, что концепция ортологии связана с различными точками видообразования, обеспечивая иерархию ортологов вдоль дерева видов.
- ОртоИнспектор [20] представляет собой хранилище ортологичных генов для 4753 организмов, охватывающих три области жизни.
- ОртологID [21] [22]
- ОртоМаМ [23] [24] [25] для млекопитающих
- ОртоMCL [26] [27]
- Округлять [28]
подходы на основе деревьев Филогенетические направлены на то, чтобы отличить видообразование от событий дупликации генов путем сравнения генных деревьев с деревьями видов, реализованных в базах данных и программных инструментах, таких как:
- ЛОФТ [29]
- ДеревоСемья [30] [31]
- Ортоискатель [32]
Третья категория гибридных подходов использует как эвристические, так и филогенетические методы для построения кластеров и определения деревьев, например:
Паралогия
[ редактировать ]Паралогичные гены — это гены, которые связаны посредством событий дупликации у последнего общего предка (LCA) сравниваемых видов. Они возникают в результате мутации дуплицированных генов во время отдельных событий видообразования. Если потомки LCA имеют мутированные гомологи исходных дуплицированных генов, то эти гены считаются паралогами. [1]
Например, в LCA один ген (ген A) может дублироваться, образуя отдельный аналогичный ген (ген B), и эти два гена будут продолжать передаваться последующим поколениям. Во время видообразования одна среда будет благоприятствовать мутации в гене А (ген А1), создавая новый вид с генами А1 и В. Затем, в отдельном событии видообразования, одна среда будет благоприятствовать мутации в гене В (ген В1), приводящей к появлению новый вид с генами А и В1. Гены потомков A1 и B1 паралогичны друг другу, поскольку они являются гомологами, связанными посредством события дупликации у последнего общего предка двух видов. [1]
Дополнительные классификации паралогов включают аллопаралоги (вне-паралоги) и симпаралоги (входящие паралоги). Аллопаралоги — это паралоги, которые произошли от дупликаций генов, предшествовавших данному событию видообразования. Другими словами, аллопаралоги — это паралоги, которые возникли в результате событий дупликации, произошедших в LCA сравниваемых организмов. Приведенный выше пример является примером аллопаралогии. Симпаралоги — это паралоги, которые развились в результате дупликации паралогичных генов в последующих событиях видообразования. В приведенном выше примере, если потомок с генами A1 и B подвергся другому событию видообразования, в котором дублировался ген A1, новый вид будет иметь гены B, A1a и A1b. В этом примере гены A1a и A1b являются симпаралогами. [1]
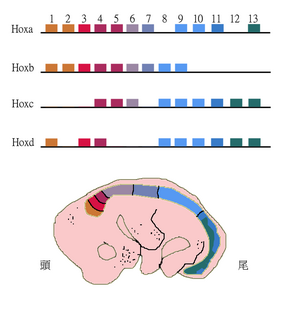
Паралогичные гены могут формировать структуру целых геномов и, таким образом, в значительной степени объяснять эволюцию генома. Примеры включают гены гомеобокса ( Hox ) у животных. Эти гены претерпели не только дупликации генов внутри хромосом , но и дупликации всего генома . В результате гены Hox у большинства позвоночных группируются на нескольких хромосомах, причем кластеры HoxAD-D являются наиболее изученными. [37]
Другим примером являются глобиновые гены, которые кодируют миоглобин и гемоглобин и считаются древними паралогами. Точно так же четыре известных класса гемоглобинов ( гемоглобин А , гемоглобин А2 , гемоглобин В и гемоглобин F ) являются паралогами друг друга. Хотя каждый из этих белков выполняет одну и ту же основную функцию транспорта кислорода, их функции уже немного различаются: фетальный гемоглобин (гемоглобин F) имеет более высокое сродство к кислороду, чем гемоглобин взрослого человека. Однако функция не всегда сохраняется. человеческий ангиогенин отделился от рибонуклеазы , и хотя эти два паралога остаются схожими по третичной структуре, их функции внутри клетки теперь совершенно различны. Например, [ нужна ссылка ]
Часто утверждается, что ортологи более функционально сходны, чем паралоги со схожей дивергенцией, но в нескольких статьях это мнение подвергается сомнению. [38] [39] [40]
Регулирование
[ редактировать ]Паралоги часто регулируются по-разному, например, за счет различных тканеспецифичных паттернов экспрессии (см. Hox-гены). Однако они также могут регулироваться по-разному на уровне белка. Например, Bacillus subtilis кодирует два паралога глутаматдегидрогеназы : GudB конститутивно транскрибируется, тогда как RocG жестко регулируется. В активном олигомерном состоянии оба фермента демонстрируют одинаковую ферментативную активность. Однако замена ферментов и промоторов приводит к серьезным потерям приспособленности, что указывает на коэволюцию промотор-фермент. Характеристика белков показывает, что по сравнению с RocG ферментативная активность GudB сильно зависит от глутамата и pH. [41]
Паралогичные хромосомные области
[ редактировать ]Иногда большие области хромосом имеют общее генное содержание, аналогичное другим хромосомным областям одного и того же генома. [42] Они хорошо охарактеризованы в геноме человека, где использовались в качестве доказательства в поддержку гипотезы 2R . Наборы дуплицированных, тройных и четырехкратных генов, родственные гены которых находятся на разных хромосомах, считаются остатками дупликаций генома или хромосом. Набор областей паралогии вместе называется паралогоном . [43] Хорошо изученные наборы областей паралогии включают области человеческой хромосомы 2, 7, 12 и 17, содержащие кластеры генов Hox , гены коллагена , гены кератина и другие дублированные гены. [44] области человеческих хромосом 4, 5, 8 и 10, содержащие гены нейропептидных рецепторов, гены гомеобокса класса NK и многие другие семейства генов , [45] [46] [47] и части хромосом человека 13, 4, 5 и X, содержащие гены ParaHox и их соседей. [48] Главный комплекс гистосовместимости (MHC) на хромосоме 6 человека имеет области паралогии на хромосомах 1, 9 и 19. [49] Большая часть человеческого генома , по-видимому, может быть отнесена к паралогичным областям. [50]
Онология
[ редактировать ]Онологичные гены — это паралогичные гены , возникшие в результате процесса дупликации целого генома . Имя было впервые дано в честь Сусуму Оно Кеном Вулфом. [51] Онологи полезны для эволюционного анализа, поскольку все онологи в геноме расходятся в течение одинакового периода времени (поскольку их общее происхождение связано с дупликацией всего генома). Также известно, что онологи демонстрируют большую связь с раком, доминантными генетическими нарушениями и вариациями числа копий патогенов. [52] [53] [54] [55] [56]
Ксенология
[ редактировать ]Гомологи, возникающие в результате горизонтального переноса генов между двумя организмами, называются ксенологами. Ксенологи могут иметь разные функции, если новая среда для горизонтально движущегося гена сильно отличается. Однако в целом ксенологи обычно выполняют схожие функции в обоих организмах. Этот термин был придуман Уолтером Фитчем. [5]
Гомеология
[ редактировать ]Гомеологичные (также называемые гомеологичными) хромосомы или части хромосом — это те, которые были собраны вместе в результате межвидовой гибридизации и аллополиплоидизации с образованием гибридного генома , и взаимоотношения которых были полностью гомологичны у предкового вида. [57] У аллополиплоидов гомологичные хромосомы в каждом родительском субгеноме должны точно спариваться во время мейоза , что приводит к дисомному наследованию; однако у некоторых аллополиплоидов гомеологичные хромосомы родительских геномов могут быть почти так же похожи друг на друга, как и гомологичные хромосомы, что приводит к тетрасомному наследованию (четыре хромосомы спариваются при мейозе), межгеномной рекомбинации и снижению фертильности. [ нужна ссылка ]
Гаметология
[ редактировать ]Гаметология обозначает отношения между гомологичными генами на нерекомбинирующих хромосомах противоположного пола . Этот термин был придуман Гарсиа-Морено и Минделлом. [58] 2000. Гаметологи возникают в результате возникновения генетического определения пола и барьеров для рекомбинации между половыми хромосомами. Примеры гаметологов включают CHDW и CHDZ у птиц. [58]
См. также
[ редактировать ]- Глубокая гомология
- EggNOG (база данных)
- ОртоБД
- Ортологическая матрица (ОМА)
- ФЕВЕР
- Белковая семья
- Белковое суперсемейство
- ДеревоСемья
- Синтелог
Ссылки
[ редактировать ]- ^ Перейти обратно: а б с д Кунин Е.В. (2005). «Ортологи, паралоги и эволюционная геномика» . Ежегодный обзор генетики . 39 : 309–38. дои : 10.1146/annurev.genet.39.073003.114725 . ПМИД 16285863 .
- ^ «Кластерный FAQ #Символы» . Кластал . Проверено 8 декабря 2014 г.
- ^ Перейти обратно: а б Рик Г.Р., де Хаэн С., Теллер Д.К., Дулиттл Р.Ф., Фитч В.М., Дикерсон Р.Э. и др. (август 1987 г.). « Гомология» в белках и нуклеиновых кислотах: терминологическая путаница и выход из нее. Клетка . 50 (5): 667. doi : 10.1016/0092-8674(87)90322-9 . ПМИД 3621342 . S2CID 42949514 .
- ^ Холман С. (январь 2004 г.). «Оценка сходства белков: упрощенная версия оценки Blast как превосходная альтернатива процентной идентичности для утверждения родов родственных белковых последовательностей» . Юридический журнал высоких технологий Санта-Клары . 21 (1): 55. ISSN 0882-3383 .
- ^ Перейти обратно: а б Fitch WM (июнь 1970 г.). «Отличение гомологичных белков от аналогичных». Систематическая зоология . 19 (2): 99–113. дои : 10.2307/2412448 . JSTOR 2412448 . ПМИД 5449325 .
Если гомология является результатом дупликации генов, так что обе копии произошли бок о бок в течение истории организма (например, гемоглобин а и b), гены следует называть паралогичными (para = параллельно). Если гомология является результатом видообразования, так что история гена отражает историю вида (например, гемоглобин у человека и мыши), гены следует называть ортологичными (орто = точные).
- ^ Фальсиаторе А., Мерендино Л., Барнеш Ф., Сеол М., Мескаускене Р., Апель К., Роше Ж.Д. (январь 2005 г.). «Белки FLP действуют как регуляторы синтеза хлорофилла в ответ на световые и пластидные сигналы у хламидомонады» . Гены и развитие . 19 (1): 176–87. дои : 10.1101/gad.321305 . ПМК 540235 . ПМИД 15630026 .
- ^ Фанг Г., Бхардвадж Н., Робилотто Р., Герштейн М.Б. (март 2010 г.). «Начало работы с ортологией генов и функциональным анализом» . PLOS Вычислительная биология . 6 (3): e1000703. Бибкод : 2010PLSCB...6E0703F . дои : 10.1371/journal.pcbi.1000703 . ПМЦ 2845645 . ПМИД 20361041 .
- ^ COG: кластеры ортологичных групп белков
Татусов Р.Л., Кунин Е.В., Липман Д.Д. (октябрь 1997 г.). «Геномный взгляд на семейства белков» . Наука . 278 (5338): 631–7. Бибкод : 1997Sci...278..631T . дои : 10.1126/science.278.5338.631 . ПМИД 9381173 . - ^ Коррейя К., Ю С.М., Махадеван Р. (январь 2019 г.). «AYbRAH: тщательно подобранная база данных ортологов дрожжей и грибов, охватывающая 600 миллионов лет эволюции» . База данных . 2019 . дои : 10.1093/база данных/baz022 . ПМЦ 6425859 . ПМИД 30893420 .
- ^ eggNOG: эволюционная генеалогия генов: неконтролируемые ортологичные группы
Мюллер Дж., Шклярчик Д., Жюльен П., Летуник И., Рот А., Кун М. и др. (январь 2010 г.). «eggNOG v2.0: расширение эволюционной генеалогии генов за счет расширенных неконтролируемых ортологичных групп, видов и функциональных аннотаций» . Исследования нуклеиновых кислот . 38 (Проблема с базой данных): D190-5. дои : 10.1093/нар/gkp951 . ПМК 2808932 . ПМИД 19900971 . - ^ Пауэлл С., Форслунд К., Шкларчик Д., Трачана К., Рот А., Уэрта-Сепас Дж. и др. (январь 2014 г.). «eggNOG v4.0: вывод вложенной ортологии для 3686 организмов» . Исследования нуклеиновых кислот . 42 (Проблема с базой данных): D231-9. дои : 10.1093/нар/gkt1253 . ПМЦ 3964997 . ПМИД 24297252 .
- ^ ГринФилДБ
Конте М.Г., Гайяр С., Ланау Н., Руар М., Перен С. (январь 2008 г.). «GreenPhylDB: база данных для сравнительной геномики растений» . Исследования нуклеиновых кислот . 36 (Проблема с базой данных): D991-8. дои : 10.1093/нар/gkm934 . ПМК 2238940 . ПМИД 17986457 . - ^ Руар М., Гиньон В., Алуом С., Лапорт М.А., Дрок Г., Вальде С. и др. (январь 2011 г.). «GreenPhylDB v2.0: сравнительная и функциональная геномика растений» . Исследования нуклеиновых кислот . 39 (Проблема с базой данных): D1095-102. дои : 10.1093/nar/gkq811 . ПМК 3013755 . ПМИД 20864446 .
- ^ Инпараноид: группы эукариотических ортологов
Остлунд Г., Шмитт Т., Форслунд К., Кёстлер Т., Мессина Д.Н., Рупра С. и др. (январь 2010 г.). «InParanoid 7: новые алгоритмы и инструменты для анализа ортологии эукариот» . Исследования нуклеиновых кислот . 38 (Проблема с базой данных): D196-203. дои : 10.1093/нар/gkp931 . ПМЦ 2808972 . ПМИД 19892828 . - ^ Зоннхаммер Э.Л., Эстлунд Г. (январь 2015 г.). «InParanoid 8: анализ ортологии между 273 протеомами, в основном эукариотическими» . Исследования нуклеиновых кислот . 43 (Проблема с базой данных): D234-9. дои : 10.1093/nar/gku1203 . ПМЦ 4383983 . ПМИД 25429972 .
- ^ Сингх П.П., Арора Дж., Исамберт Х. (июль 2015 г.). «Идентификация генов онологов, происходящих в результате дупликации всего генома у ранних позвоночных, на основе сравнения синтении нескольких геномов» . PLOS Вычислительная биология . 11 (7): e1004394. Бибкод : 2015PLSCB..11E4394S . дои : 10.1371/journal.pcbi.1004394 . ПМК 4504502 . ПМИД 26181593 .
- ^ «Позвоночные онологи» . ohnologs.curie.fr . Проверено 12 октября 2018 г.
- ^ Альтенхофф А.М., Гловер Н.М., Трейн К.М., Калеб К., Уорвик Вестроци А., Дилус Д. и др. (январь 2018 г.). «База данных ортологии OMA в 2018 году: обнаружение эволюционных взаимосвязей между всеми сферами жизни с помощью более богатых веб- и программных интерфейсов» . Исследования нуклеиновых кислот . 46 (Д1): Д477–Д485. дои : 10.1093/нар/gkx1019 . ПМЦ 5753216 . ПМИД 29106550 .
- ^ Здобнов Е.М., Тегенфельдт Ф., Кузнецов Д., Уотерхаус Р.М., Симау Ф.А., Иоаннидис П. и др. (январь 2017 г.). «OrthoDB v9.1: каталогизация эволюционных и функциональных аннотаций для ортологов животных, грибов, растений, архей, бактерий и вирусов» . Исследования нуклеиновых кислот . 45 (Д1): Д744–Д749. дои : 10.1093/nar/gkw1119 . ПМК 5210582 . ПМИД 27899580 .
- ^ Неверс Ю., Кресс А., Дефоссет А., Рипп Р., Линард Б., Томпсон Дж.Д. и др. (январь 2019 г.). «ОртоИнспектор 3.0: открытый портал сравнительной геномики» . Исследования нуклеиновых кислот . 47 (Д1): Д411–Д418. дои : 10.1093/nar/gky1068 . ПМК 6323921 . ПМИД 30380106 .
- ^ ОртологИД
Чиу Дж.К., Ли Э.К., Иган М.Г., Саркар И.Н., Коруцци Г.М., ДеСалле Р. (март 2006 г.). «OrthologID: автоматизация идентификации ортологов в масштабе генома в рамках экономичности» . Биоинформатика . 22 (6): 699–707. doi : 10.1093/биоинформатика/btk040 . ПМИД 16410324 . - ^ Иган М., Ли Э.К., Чиу Дж.К., Коруцци Дж., Десалле Р. (2009). «Оценка ортологии генов с помощью OrthologID». В Посаде Д (ред.). Биоинформатика для анализа последовательностей ДНК . Методы молекулярной биологии. Том. 537. Хумана Пресс. стр. 23–38. дои : 10.1007/978-1-59745-251-9_2 . ISBN 978-1-59745-251-9 . ПМИД 19378138 .
- ^ ОртоМаМ
Ранвез В., Дельсук Ф., Ранвез С., Белхир К., Тилак М.К., Дузери Э.Дж. (ноябрь 2007 г.). «OrthoMaM: база данных ортологичных геномных маркеров для филогенетики плацентарных млекопитающих» . Эволюционная биология BMC . 7 (1): 241. Бибкод : 2007BMCEE...7..241R . дои : 10.1186/1471-2148-7-241 . ПМК 2249597 . ПМИД 18053139 . - ^ Дузери Э.Дж., Скорнавакка К., Ромигье Дж., Белкхир К., Галтье Н., Дельсук Ф., Ранвез В. (июль 2014 г.). «OrthoMaM v8: база данных ортологичных экзонов и кодирующих последовательностей для сравнительной геномики млекопитающих» . Молекулярная биология и эволюция . 31 (7): 1923–8. дои : 10.1093/molbev/msu132 . ПМИД 24723423 .
- ^ Скорнавакка К., Белхир К., Лопес Дж., Дернат Р., Дельсук Ф., Дузери Э.Дж., Ранвез В. (апрель 2019 г.). «OrthoMaM v10: увеличение масштаба ортологической кодирующей последовательности и выравнивания экзонов с использованием более чем ста геномов млекопитающих» . Молекулярная биология и эволюция . 36 (4): 861–862. дои : 10.1093/molbev/msz015 . ПМК 6445298 . ПМИД 30698751 .
- ^ OrthoMCL: Идентификация групп ортологов для геномов эукариот
Чен Ф., Макки А.Дж., Стокерт С.Дж., Роос Д.С. (январь 2006 г.). «OrthoMCL-DB: запрос к обширной многовидовой коллекции групп ортологов» . Исследования нуклеиновых кислот . 34 (Проблема с базой данных): D363-8. дои : 10.1093/нар/gkj123 . ПМЦ 1347485 . ПМИД 16381887 . - ^ Фишер С., Бранк Б.П., Чен Ф., Гао X, Харб О.С., Йодис Дж.Б. и др. (сентябрь 2011 г.). «Использование OrthoMCL для отнесения белков к группам OrthoMCL-DB или для кластеризации протеомов в новые группы ортологов» . Современные протоколы в биоинформатике . Глава 6 (1): Раздел 6.12.1–19. дои : 10.1002/0471250953.bi0612s35 . ISBN 978-0471250951 . ПМК 3196566 . ПМИД 21901743 .
- ^ Сводка новостей
Делука Т.Ф., Ву И.Х., Пу Дж., Монаган Т., Пешкин Л., Сингх С., Уолл Д.П. (август 2006 г.). «Сводка новостей: мультигеномное хранилище ортологов и эволюционных расстояний» . Биоинформатика . 22 (16): 2044–6. doi : 10.1093/биоинформатика/btl286 . ПМИД 16777906 . - ^ TreeFam: база данных семейств деревьев.
ван дер Хейден Р.Т., Снел Б., ван Ноорт В., Хюйнен М.А. (март 2007 г.). «Прогнозирование ортологии с масштабируемым разрешением посредством анализа филогенетического дерева» . БМК Биоинформатика . 8:83 . дои : 10.1186/1471-2105-8-83 . ПМЦ 1838432 . ПМИД 17346331 . - ^ TreeFam: база данных семейств деревьев.
Жуан Дж., Ли Х., Чен З., Коглан А., Коин Л.Дж., Го Ю и др. (январь 2008 г.). «TreeFam: Обновление 2008 года» . Исследования нуклеиновых кислот . 36 (Проблема с базой данных): D735-40. дои : 10.1093/нар/gkm1005 . ПМК 2238856 . ПМИД 18056084 . - ^ Шрайбер Ф., Патрисио М., Муффато М., Пиньятелли М., Бейтман А. (январь 2014 г.). «TreeFam v9: новый веб-сайт, больше видов и ортология на лету» . Исследования нуклеиновых кислот . 42 (Проблема с базой данных): D922-5. дои : 10.1093/нар/gkt1055 . ПМЦ 3965059 . ПМИД 24194607 .
- ^ OrthoFinder: ортологи генных деревьев.
Эммс Д.М., Келли С. (ноябрь 2019 г.). «OrthoFinder: вывод филогенетической ортологии для сравнительной геномики» . Геномная биология . 20 (1): 238. doi : 10.1186/s13059-019-1832-y . ПМЦ 6857279 . ПМИД 31727128 . - ^ Вилелла А.Дж., Северин Дж., Урета-Видал А., Хенг Л., Дурбин Р., Бирни Э. (февраль 2009 г.). «EnsemblCompara GeneTrees: Полные филогенетические деревья позвоночных с учетом дублирования» . Геномные исследования . 19 (2): 327–35. дои : 10.1101/гр.073585.107 . ПМЦ 2652215 . ПМИД 19029536 .
- ^ Спасибо А.С., Соранзо Н., Хаэрти В., Дэйви Р.П. (март 2018 г.). «GeneSeqToFamily: рабочий процесс Galaxy для поиска семейств генов на основе конвейера Ensembl Compara GeneTrees» . ГигаСайенс . 7 (3): 1–10. doi : 10.1093/gigascience/giy005 . ПМК 5863215 . ПМИД 29425291 .
- ^ Сэйерс Э.В., Барретт Т., Бенсон Д.А., Болтон Э., Брайант Ш., Канезе К. и др. (январь 2011 г.). «Ресурсы базы данных Национального центра биотехнологической информации» . Исследования нуклеиновых кислот . 39 (Проблема с базой данных): D38-51. дои : 10.1093/nar/gkq1172 . ПМК 3013733 . ПМИД 21097890 .
- ^ Фултон Д.Л., Ли Ю.Й., Лэрд М.Р., Хорсман Б.Г., Рош Ф.М., Бринкман Ф.С. (май 2006 г.). «Повышение специфичности высокопроизводительного прогнозирования ортологов» . БМК Биоинформатика . 7 : 270. дои : 10.1186/1471-2105-7-270 . ПМЦ 1524997 . ПМИД 16729895 .
- ^ Перейти обратно: а б Закани Дж., Дюбул Д. (август 2007 г.). «Роль Hox-генов в развитии конечностей позвоночных». Текущее мнение в области генетики и развития . 17 (4): 359–66. дои : 10.1016/j.где.2007.05.011 . ПМИД 17644373 .
- ^ Студер Р.А., Робинсон-Речави М (май 2009 г.). «Насколько мы можем быть уверены в том, что ортологи похожи, а паралоги различаются?» . Тенденции в генетике . 25 (5): 210–6. дои : 10.1016/j.tig.2009.03.004 . ПМИД 19368988 .
- ^ Нерт Н.Л., Кларк В.Т., Радивояк П., Хан М.В. (июнь 2011 г.). «Проверка гипотезы об ортологе с помощью сравнительных функциональных геномных данных млекопитающих» . PLOS Вычислительная биология . 7 (6): e1002073. Бибкод : 2011PLSCB...7E2073N . дои : 10.1371/journal.pcbi.1002073 . ПМК 3111532 . ПМИД 21695233 .
- ^ Эйзен Дж. (20 сентября 2011 г.). «Специальный гостевой пост и приглашение на обсуждение от Мэтью Хана по статье с гипотезами ортологов» .
- ^ Нода-Гарсия Л., Ромеро Ромеро М.Л., Лонго Л.М., Колодкин-Гал И., Тауфик Д.С. (июль 2017 г.). «Глутаматдегидрогеназы бацилл разошлись в результате совместной эволюции транскрипции и регуляции ферментов» . Отчеты ЭМБО . 18 (7): 1139–1149. дои : 10.15252/эмбр.201743990 . ПМК 5494520 . ПМИД 28468957 .
- ^ Лундин Л.Г. (апрель 1993 г.). «Эволюция генома позвоночных, отраженная в паралогичных хромосомных областях человека и домовой мыши». Геномика . 16 (1): 1–19. дои : 10.1006/geno.1993.1133 . PMID 8486346 .
- ^ Кулиер Ф., Попович С., Вилле Р., Бирнбаум Д. (декабрь 2000 г.). «Кластеры генов MetaHox». Журнал экспериментальной зоологии . 288 (4): 345–51. doi : 10.1002/1097-010X(20001215)288:4<345::AID-JEZ7>3.0.CO;2-Y . ПМИД 11144283 .
- ^ Раддл Ф.Х., Бентли К.Л., Мурта М.Т., Риш Н. (1994). «Потеря и приобретение генов в эволюции позвоночных». Разработка . 1994 : 155–61. doi : 10.1242/dev.1994.Supplement.155 . ПМИД 7579516 .
- ^ Пебуск М.Дж., Кулиер Ф., Бирнбаум Д., Понтаротти П. (сентябрь 1998 г.). «Древние крупномасштабные дупликации генома: филогенетический анализ и анализ сцепления проливают свет на эволюцию генома хордовых» . Молекулярная биология и эволюция . 15 (9): 1145–59. doi : 10.1093/oxfordjournals.molbev.a026022 . ПМИД 9729879 .
- ^ Ларссон Т.А., Олссон Ф., Сундстрем Г., Лундин Л.Г., Бреннер С., Венкатеш Б., Лархаммар Д. (июнь 2008 г.). «Ранние дупликации хромосом позвоночных и эволюция областей гена рецептора нейропептида Y» . Эволюционная биология BMC . 8 (1): 184. Бибкод : 2008BMCEE...8..184L . дои : 10.1186/1471-2148-8-184 . ПМЦ 2453138 . ПМИД 18578868 .
- ^ Поллард С.Л., Голландия PW (сентябрь 2000 г.). «Доказательства наличия 14 кластеров гомеобоксных генов в происхождении генома человека» . Современная биология . 10 (17): 1059–62. дои : 10.1016/S0960-9822(00)00676-X . ПМИД 10996074 . S2CID 32135432 .
- ^ Малли Дж. Ф., Чиу Ч., Голландия П. В. (июль 2006 г.). «Распад кластера гомеобокса после дупликации генома костистых рыб» . Труды Национальной академии наук Соединенных Штатов Америки . 103 (27): 10369–10372. Бибкод : 2006PNAS..10310369M . дои : 10.1073/pnas.0600341103 . ПМК 1502464 . ПМИД 16801555 .
- ^ Флажник М.Ф., Касахара М. (сентябрь 2001 г.). «Сравнительная геномика MHC: взгляд на эволюцию адаптивной иммунной системы» . Иммунитет . 15 (3): 351–62. дои : 10.1016/S1074-7613(01)00198-4 . ПМИД 11567626 .
- ^ МакЛисахт А., Хокамп К., Вульф К.Х. (июнь 2002 г.). «Обширное геномное дупликация во время ранней эволюции хордовых». Природная генетика . 31 (2): 200–4. дои : 10.1038/ng884 . ПМИД 12032567 . S2CID 8263376 .
- ^ Вулф К. (май 2000 г.). «Надежность — это не то, о чем вы думаете». Природная генетика . 25 (1): 3–4. дои : 10.1038/75560 . ПМИД 10802639 . S2CID 85257685 .
- ^ Сингх П.П., Аффельдт С., Касконе И., Селимоглу Р., Камонис Дж., Исамберт Х. (ноябрь 2012 г.). «О расширении репертуара «опасных» генов путем полногеномной дупликации у ранних позвоночных» . Отчеты по ячейкам . 2 (5): 1387–98. дои : 10.1016/j.celrep.2012.09.034 . ПМИД 23168259 .
- ^ Малагути Дж., Сингх П.П., Исамберт Х. (май 2014 г.). «О сохранении дубликатов генов, склонных к доминантным вредным мутациям» . Теоретическая популяционная биология . 93 : 38–51. дои : 10.1016/j.tpb.2014.01.004 . ПМИД 24530892 .
- ^ Сингх П.П., Аффельдт С., Малагути Г., Исамберт Х. (июль 2014 г.). «Гены доминантных заболеваний человека обогащены паралогами, возникающими в результате полногеномной дупликации» . PLOS Вычислительная биология . 10 (7): e1003754. Бибкод : 2014PLSCB..10E3754S . дои : 10.1371/journal.pcbi.1003754 . ПМЦ 4117431 . ПМИД 25080083 .
- ^ МакЛисахт А., Макино Т., Грейтон Х.М., Тропеано М., Митчелл К.Дж., Вассос Э., Коллиер Д.А. (январь 2014 г.). «Онологи чрезмерно представлены в патогенных мутациях числа копий» . Труды Национальной академии наук Соединенных Штатов Америки . 111 (1): 361–6. Бибкод : 2014PNAS..111..361M . дои : 10.1073/pnas.1309324111 . ПМЦ 3890797 . ПМИД 24368850 .
- ^ Макино Т., Маклизат А. (май 2010 г.). «Онологи в геноме человека сбалансированы по дозировке и часто связаны с болезнями» . Труды Национальной академии наук Соединенных Штатов Америки . 107 (20): 9270–4. Бибкод : 2010PNAS..107.9270M . дои : 10.1073/pnas.0914697107 . ПМК 2889102 . ПМИД 20439718 .
- ^ Гловер Н.М., Редестиг Х., Дессимоз С. (июль 2016 г.). «Гомеологи: что это такое и как мы их определяем?» . Тенденции в науке о растениях . 21 (7). Cell Press : 609–621. doi : 10.1016/j.tplants.2016.02.005 . ПМЦ 4920642 . ПМИД 27021699 .
- ^ Перейти обратно: а б Гарсиа-Морено Дж., Минделл Д.П. (декабрь 2000 г.). «Укоренение филогении с гомологичными генами на противоположных половых хромосомах (гаметологах): тематическое исследование с использованием птичьего ИБС» . Молекулярная биология и эволюция . 17 (12): 1826–32. doi : 10.1093/oxfordjournals.molbev.a026283 . ПМИД 11110898 .


